Pima Indians diabetes dataset 考古溯源 & model prediction
Machine learning常用到的一个diabetes 糖尿病资料集,Pima印第安人数据起源於1980年代,目前在机器学习领域还是广为使用,在Kaggle上的运用范例就超过了1700个以上。
我们今天就来探究一下这个资料集。
<资料集来源>:Kaggle download here
from National Institute of Diabetes and Digestive and Kidney Diseases; Includes cost data (donated by Peter Turney)
<资料集说明>来源
768笔记录。 9个栏位:8 特徵 1 target
This dataset describes the medical records for Pima Indians and whether or not each patient will have an onset of diabetes within five years.
Fields description follow:
- Preg = Number of times pregnant
- Glucose = Plasma glucose concentration a 2 hours in an oral glucose tolerance test
- BP = Diastolic blood pressure (mm Hg)
- Skin = Triceps skin fold thickness (mm)
- Insulin = 2-Hour serum insulin (mu U/ml)
- BMI = Body mass index (weight in kg/(height in m)^2)
- Pedi = Diabetes pedigree function
- Age = Age (years)
- Class = Class variable (1:tested positive for diabetes, 0: tested negative for diabetes)
< 资料集溯源 >
我们研读一下原创文献,是如何解释他们的材料方法。
文献标题:Using the ADAP Learning Algorithm to Forecast the Onset of Diabetes Mellitus
此研究是由The National Institute of Diabetes Digestive and Kidney Diseases、The Johns Hopkins University School of Medicine共同发表
1988年原创者文献出处:
Proc Annu Symp Comput Appl Med Care. 1988 Nov 9 : 261–265.
8项特徵值之中,比较让人疑惑的是Diabetes pedigree function (糖尿病族谱系数DPF)的定义与计算方法,A function that scores the likelihood of diabetes based on family history.
我们先把该篇原创论文,摘要的说一遍。
<研究动机>
在糖尿病高风险的Pima印第安人族群中,运用ADAP algorithm(一种早期的neural network model),测试此一方法对於糖尿病发病的预测能力。
<研究族群>
Pima印第安人(Phoenix, Arizona)是一批糖尿病高风险发病的族群,该族群居民自1965年起每隔两年都会接受身体检查。如果”口服葡萄糖耐受测试”(oral glucose tolerance test)後的2小时血糖数值,高於200 mg/dl 即视为糖尿病患者。
< 变数选择 > 8项input variables
- Number of times pregnant 怀孕次数
- Plasma Glucose Concentration at 2 Hours in an Oral Tolerance Test (GTT) 口服葡萄糖耐受测试後2小时的血糖数据
- Diastolic Blood pressure 血压(舒张压) mmHg
- Triceps Skin Fold Thickness (mm) 肱三头肌皮肤厚度
- 2-Hour Serum Insulin 2小时後血清胰岛素数据
- Body mass index BMI
- Diabetes Pedigree Function族谱系数
- Age (years)年龄
Diabetes Pedigree Function 族谱系数 DPF,此一参数是他们自创的。文中有解释计算方式,有兴趣的请自行参阅。
大致意思是:如果家族中得病的人数较多,而这些人发病的年龄比较早,或者亲等关系比较近的,这个DPF数值就会比较高。反之,则DPF数值比较低。
公式大略是以”亲属发病年龄”、”亲等关系比例”…等参数加权计算出来的。
< Case selection >案例选择,必须全部符合以下四项标准:
- 女性
- 受测时年龄大於(含)21岁
- 五年内被诊断出糖尿病者,或者接受GTT口服葡萄糖耐受测试後五年内(或以上)都没有糖尿病者。(这段是我会错意了,文末会说明)
- 如果受测後一年内诊断出糖尿病者,此记录不采用,剔除研究对象。因为这些数据倾向於比较好预测。
最後,train组 576例,test组192例,共计768例。
< ADAP > 作者解释ADAP algorithm作法,我们就不讨论了。
< 资料集表达什麽? >
2014年有篇文章 The Open Diabetes Journal, 2014, 7, 5-13 特讨分析这笔Pima Dataset 得出如下结论:
- Triceps skin fold thickness与PGL(血糖值)有显着的”负相关”
- 2-hr insulin与PGL有显着的”正相关”
- BMI body mass index与PGL有显着的”正相关”
- Diabetes pedigree function与PGL有显着的”正相关”
- Age与PGL有显着的”正相关”
- PGL is independent of number of times pregnant and diastolic blood pressure
我们今天的重点,就是来分析此一资料集,看看能否视觉化,重现上述的相关性,并做modeling、prediction预测
Step1. Read dataset / Explore
''' Step1. Load dataset / explore '''
df = pd.read_csv('pimaDM.csv')
df.isnull().sum()
df.describe()
df.info()
df.head()
df.value_counts()
Step 2. data visulalize 画个Box图 观察离散程度
df0 无病组 df1 有病组 把2组画在一起
''' Step 2. data visulalize
画个Box图 观察离散程度 '''
# df0 无病组 df1 有病组
df0 = df[df['Class'] == 0 ]
df1 = df[df['Class'] == 1 ]
# 把2组画在一起
fig,axes = plt.subplots(1,2,sharey=True,figsize=(10,6))
axes[0].set_title('Healthy')
axes[1].set_title('DM')
fig.autofmt_xdate(rotation=45)
sns.boxplot(data=df0,ax=axes[0])
sns.boxplot(data=df1,ax=axes[1])
fig.savefig('DM_orig_box.jpg')
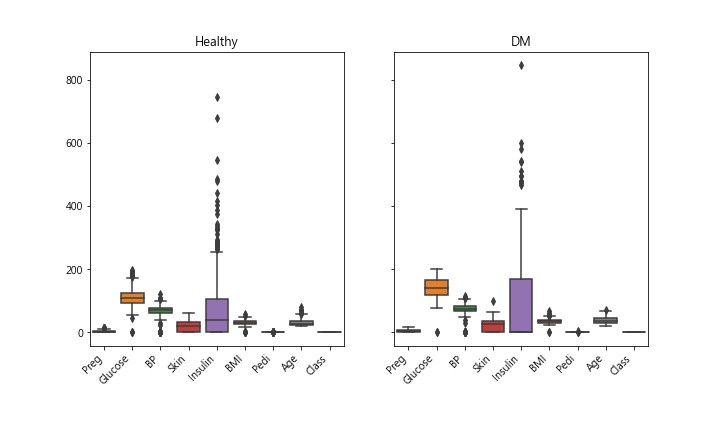
Insulin此特徵数据,离群值似乎很多。算一下统计数据看看
''' Step 3. 统计数据 '''
pd.set_option('display.max_columns',None) # 显示所有columns
print(df.describe())
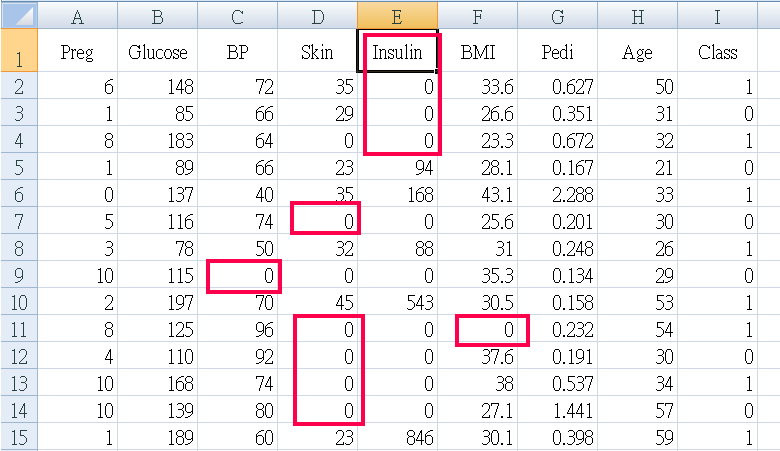
天啊! 出现了很多不合理数据,怎麽说? BP血压是0 ? 皮肤厚度是0 ? 不可能是0,应该是当时没做测量,就随意给个0当数字。
Step 4. 不合理的异常数据处理
血压、皮肤厚度...多项多笔数据=0 明显不合理,将五项特徵 Glucose BP Skin Insulin BMI 数据=0 剔除 ( ps. 原本还包括异常值大於95percentile者,但是资料只剩下三分之一了)
''' Step 4. 不合理的异常数据处理
血压、皮肤厚度...多项多笔数据=0 明显不合理
将五项特徵 Glucose BP Skin Insulin BMI
数据=0 and >95percentile者剔除
'''
df_Trim = df # 处理dataframe
# 95 percentile
#Insulin_q95 = df_Trim['Insulin'].quantile(.95)
#print(f'Insulin 95 percentlie: {Insulin_q95}')
#idxNames = df_Trim[ df_Trim['Insulin'] >= Insulin_q95 ].index
#df_Trim = df.drop(idxNames)
# = 0 者
idxNames = df_Trim[ df_Trim['Insulin']<=0 ].index
df_Trim = df_Trim.drop(idxNames)
print(df_Trim.info())
print(df_Trim)
#---以下略---
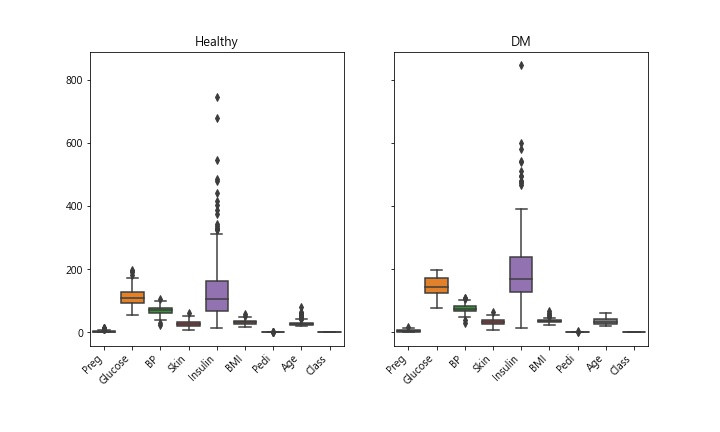
Step 5. 剩下的资料,再画一次 boxplot
剔除 0 & >95percentile者,剩下 273笔记录 768笔 剩下 35.5% 可用, 如果只剔除 0者,则剩下 392笔记录
< 检视资料 > 用EXCEL检视剩下的资料,虾米!
全部的案例(有病、无病的)“血糖值都小於200”?
糖尿病的定义不是要血糖值大於200吗? 我抓错资料了吗?
再进去Kaggle看看原始资料集。
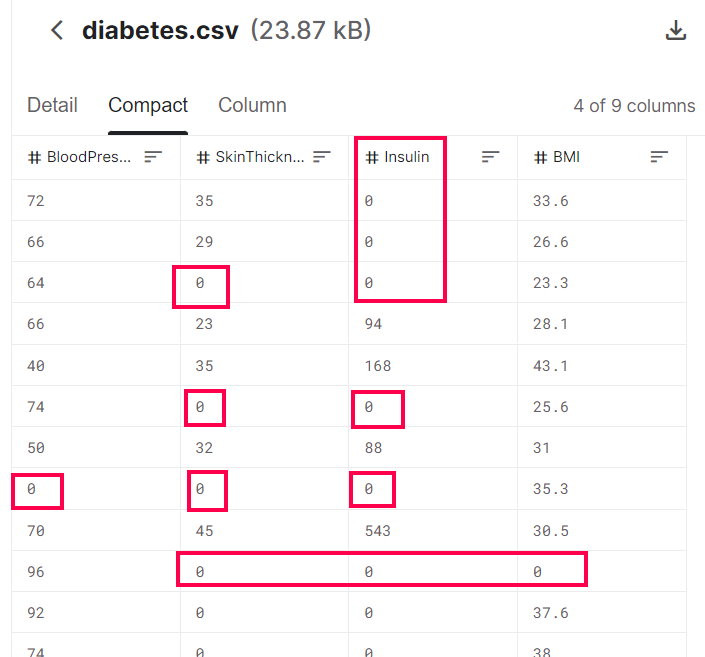
没错,Kaggle上的资料集和我的是一样的,也都是小於200,Why ?
回头再详细看一看原创文献,Case selection第3项:
Only one examination was selected per subject. 每人只选用一次检验值
That examination was one that revealed a non-diabetic GTT and met one of the following two criteria: 该次检验是在”葡萄糖耐受测试”显示为”非糖尿病”的那次,同时符合以下两标准者:
- Diabetes was diagnosed within five years of the examination, OR 五年内被诊断出糖尿病,或者
- A GTT performed five or more years later failed to reveal diabetes mellitus. 5年内(以上)所做的”葡萄糖耐受测试”没有显示出有病者
原来如此,所以,资料集里面的”血糖值”都是正常范围内的,也就是病人”还没被诊断出糖尿病之前”的数据。这就很难理解,这些数据并不是直观的”实验组”、”对照组”的特徵资料,而是”有病者,发病以前的资料”+”没病者的资料”。
所以,该文章作者的方法是:使用”未发病前”的资料去预测以後是否会发病。
说实话,这样的实验设计有点难理解,而且执行上也不容易。
必须要在同一个社区(族群)内,长期追踪同一群人5年以上,收案不易、数据测量也不易齐全。
另外,我们再回头看看上面2014年那篇,好像价值性就没有那麽高了。因为他们在一群正常数据的人(都是未发病前数据)之中发现血糖与其它项特徵值有正(负)相关,但是却没着墨於”预测”。毕竟原创资料集其目的是在於”预测”,而不是看特徵值之”趋势”、”相关”。
Step 6. Prediction
终於,要来使用资料集了。这个资料集去除了不合理的数值後(应该是当时没做测量,就给个0),剩下392笔可用,只占原本768笔的一半。
经过上面冗长的考古之後,我们就选两种方法来建立模型、预测吧。
LogisticRegression、RandomForest
直接进代码吧
- 准备资料,设定 X ,y
- Build the Model : training
- 评估模型准确度 两种model的accuracy
- 储存模型
''' Step 6. 准备资料,设定 X ,y '''
from sklearn.model_selection import train_test_split
from sklearn.preprocessing import StandardScaler
y = df_Trim['Class'] # y 诊断结果= Class
''' 去除 target栏位,留下特徵栏位-->X '''
X = df_Trim.drop(['Class'], axis = 1)
print(X.shape)
print(X.head(5)) # X is a dataframe
print(y[:5]) # y is a Series
# split dataset
X_train, X_test, y_train, y_test = train_test_split(X, y,
test_size=0.2,
stratify=y,
random_state=0)
#print(len(X_train),len(X_test))
''' Step 7. Build the Model : training'''
# model logistic regression
from sklearn.linear_model import LogisticRegression
logis = LogisticRegression(solver='lbfgs',max_iter = 400)
logis.fit(X_train, y_train)
# model random forest
from sklearn.ensemble import RandomForestClassifier
fores = RandomForestClassifier()
fores.fit(X_train, y_train)
''' Step 8. 评估模型准确度 两种model的accuracy '''
from sklearn.metrics import accuracy_score
pred_logis = logis.predict(X_test)
pred_fores = fores.predict(X_test)
a1 = accuracy_score(pred_logis, y_test)
a2 = accuracy_score(pred_fores, y_test)
print(f'两种模型的准确率 accuracy: logis: {a1} fores: {a2}')
''' Step 9. 储存模型 '''
import pickle
mdl_DMlr = 'DMlr.model'
pickle.dump(logis, open(mdl_DMlr, 'wb'))
mdl_DMfs = 'DMfs.model'
pickle.dump(fores, open(mdl_DMfs, 'wb'))
print(' 建模完成 models saved ')
写个py,使用模型预测
""" PimaDM_ModelUse.py 2021-09-14 neoCaffe
使用建立好的模型,进行诊断预测 diabetes
从 PimaDM.csv取两笔,预测是否发病
"""
print(__doc__)
import pandas as pd
import random
import pickle
''' 载入资料集 '''
df = pd.read_csv('pimaDM.csv')
r,c = df.shape
''' 任意取两笔 '''
n = random.randint(0,r)
test1 = list(df.iloc[n].values)
m = random.randint(0,r)
test2 = list(df.iloc[m].values)
# 真正的诊断
Dx1 = test1[-1]
Dx2 = test2[-1]
# 特徵值
test1 = [test1[:-1]]
test2 = [test2[:-1]]
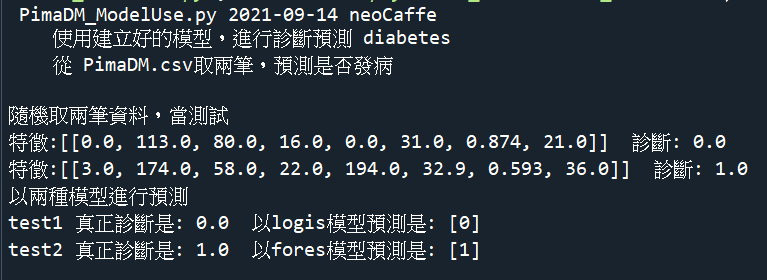
print('随机取两笔资料,当测试')
print(f'特徵:{test1} 诊断: {Dx1}')
print(f'特徵:{test2} 诊断: {Dx2}')
''' 以两种模型进行预测 '''
print('以两种模型进行预测''')
mdl_logis = pickle.load(open('DMlr.model', 'rb'))
predict1 = mdl_logis.predict(test1)
mdl_fores = pickle.load(open('DMfs.model', 'rb'))
predict2 = mdl_fores.predict(test2)
print(f'test1 真正诊断是: {Dx1} 以logis模型预测是: {predict1}')
print(f'test2 真正诊断是: {Dx2} 以fores模型预测是: {predict2}')
成果画面
结案收工,以上程序码在GitHub
< source code+csv download GitHub >
[Day18] Operations Suite
今天我们来介绍云端的监控, Cloud Operations Suite 。这个服务以前被称做 St...
Day 6:Hello....iOS world! 建立第一个KMM专案(iOS)
Keyword:Xcode,simulator 到Day6完成第一个KMM专案的Code放在 KMM...
Day 22 来写一个简单e2e测试
今天我们来写一个简单的form来当作测试吧,首先我们刻出一个简单的画面 const App: FC ...
008-工作心得
今天不想提软件相关的心得,想来聊一点工作沟通相关的事情。在开始分享之前,必须要先提到,我知道自己不是...
[Day10]字符函数
字符函数,又分为大小写转换函数及字符处理函数。 大小写转换函数: 字符处理函数: 下篇会从日期单列函...